Cytometry and Cell Sorting Core Facility
Die Cytometry and Cell Sorting Core Facility stellt Forschenden modernste Technologien für die Durchflusszytometrie und das Zellsortieren zur Verfügung. Sie ist ausgestattet mit:
Analyzer (5)
-
A3 (HCTI Raum 04.2.022)
Software:
- DIVA
Laser:
- UV Laser: 355 nm
- violetter Laser: 405 nm
- blauer Laser: 488 nm
- grüner Laser: 561 nm
- roter Laser: 633 nm
Detektoren:
- FSC + SSC
- 29 Fluoreszenzkanäle
Es ist die Bearbeitung folgender Proben möglich: S0, S1, S2. Es dürfen keine HIV-positiven oder Hepatitis-B oder -C positiven Proben gemessen werden. Daher müssen primäre humane Proben vorher darauf getestet werden oder die Proben müssen fixiert werden.
-
Quanteon (CF1 Raum 0.068)
Software:
- NovoExpress
Laser:
- violetter Laser: 405 nm
- blauer Laser: 488 nm
- grüner Laser: 561 nm
- roter Laser: 637 nm
Detektoren:
- FSC + SSC
- 16 Fluoreszenzkanäle
Besondere Ausstattung:
- Verwendung von 96-Wellplatten möglich
- Verwendung eines Tuberacks zum automatischen Messen möglich
- Bestimmung von absoluten Zellzahlen
- Software enthält Programme zur Erstellung von Zellzyklus- und Proliferationsanalysen
Es ist die Bearbeitung folgender Proben möglich: S0, S1, S2. Es dürfen keine HIV-positiven oder Hepatitis-B oder -C positiven Proben gemessen werden. Daher müssen primäre humane Proben vorher darauf getestet werden oder die Proben müssen fixiert werden.
-
LSR Fortessa mit 4 Lasern (CF1 Raum 0.068)
Software:
- DIVA
Laser:
- violetter Laser: 405 nm
- blauer Laser: 488 nm
- grüner Laser: 561 nm
- roter Laser: 640 nm
Detektoren:
- FSC + SSC
- 17 Fluoreszenzkanäle
Besondere Ausstattung:
- HTS zum Messen aus 96-Wellplatten
Es ist die Bearbeitung folgender Proben möglich: S0, S1, S2. Es dürfen keine HIV positiven oder Hepatitis-B oder -C positiven Proben gemessen werden. Daher müssen primäre humane Proben vorher darauf getestet werden oder die Proben müssen fixiert werden.
-
LSR Fortessa mit 5 Lasern (CF1 Raum 0.068)
Software:
- DIVA
Laser:
- UV Laser: 355 nm
- violetter Laser: 405 nm
- blauer Laser: 488 nm
- grüner Laser: 561 nm
- roter Laser: 640 nm
Detektoren:
- FSC + SSC
- 18 Fluoreszenzkanäle
Es ist die Bearbeitung folgender Proben möglich: S0, S1, S2. Es dürfen keine HIV positiven oder Hepatitis-B oder -C positiven Proben gemessen werden. Daher müssen primäre humane Proben vorher darauf getestet werden oder die Proben müssen fixiert werden.
-
Aurora (HCTI Raum 04.2.022)
Für hoch komplexe Applikationen steht der Aurora als Highend-Durchflusszytometer in der Core Facility zur Verfügung. Das Gerät bietet zu den 3 Standardlasern noch einen gelb-grünen und einen UV-Laser. Da es sich um ein Spektralgerät (64 Fluoreszenz-Kanäle + 3 Scatter-Kanäle) handelt, können auch Farbstoffe, die ähnliche Emissionsspektren haben getrennt werden.
Das Ergebnis von Proben mit hoher Autofluoreszenz kann durch den Abzug der Autofluoreszenz verbessert werden.Messungen können selbständig bzw. als Dienstleistung durch die Core Unit durchgeführt werden.
Es ist die Bearbeitung folgender Proben möglich: S0, S1, S2. Es dürfen keine HIV-positiven oder Hepatitis-B oder -C positiven Proben gemessen werden. Daher müssen primäre humane Proben vorher darauf getestet werden oder die Proben müssen fixiert werden.
Das Gerät ist mit folgenden Lasern ausgestattet:
- 355 nm: UV-Laser
- 405 nm: violetter Laser
- 488 nm: blauer Laser
- 561 nm: grüner Laser
- 640 nm: roter Laser
Sorter (3)
-
S6 SE (HCTI Raum 04.2.022) 6-fach-Sortierung, spektral, 5 Laser , ungetestete humane Primärproben möglich
Software:
- DIVA
Laser:
- UV Laser: 355 nm
- violetter Laser: 405 nm
- blauer Laser: 488 nm
- grüner Laser: 561 nm
- roter Laser: 637 nm
Detektoren:
- 2 SSC
- 48 Fluoreszenzkanäle
Außerdem bietet es folgende neue Funktionen:
- 6-fach Sortierung
- spektrales Unmixing
Der Sorter steht in einer Sterilwerkbank, so dass auch ungetestete humane Primärproben sortiert werden können.
-
AriaIllu (CF1 Raum 0.068.1) 4-fach-Sortierung, 4 Laser, ungetestete humane Primärproben nicht möglich
Software:
- DIVA
Laser:
- violetter Laser: 407 nm
- blauer Laser: 488 nm
- grüner Laser: 561 nm
- roter Laser: 633 nm
Detektoren:
- FSC + SSC
- 13 Fluoreszenzkanäle
Außerdem bietet es folgende Funktionen:
- Auftrennung von GFP und YFP möglich ohne das Tauschen von Filtern
-
AriaFusion (CF1 Raum 0.068.1) 4-fach-Sortierung, 5 Laser, ungetestete humane Primärproben möglich
Software:
- DIVA
Laser:
- UV Laser: 355 nm
- violetter Laser: 405 nm
- blauer Laser: 488 nm
- grüner Laser: 561 nm
- roter Laser: 640 nm
Detektoren:
- FSC + SSC
- 18 Fluoreszenzkanäle
Der Sorter steht in einer Sterilwerkbank, so dass auch ungetestete humane Primärproben sortiert werden können.
-
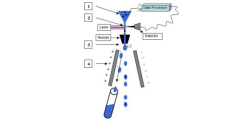
FACS Sorting - Das Prinzip
1. Die Zellen werden durch einen Hüllstrom wie Perlen an einer Schnur aufgereiht (hydrodynamische Fokussierung)
2. Im Laserschnittpunkt findet die Analyse der Zellen statt.
3. Die Nozzle trennt den Strahl in einzelne Tropfen und lädt die zu sortierenden Tropfen auf.
4. Die aufgeladenen Tropfen werden im elektrischen Feld abgelenkt und fallen in das entsprechende Auffanggefäß.
-
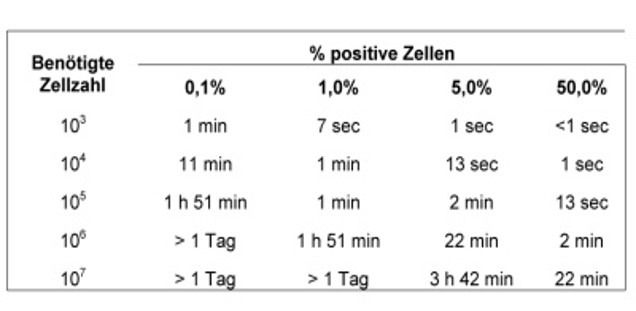
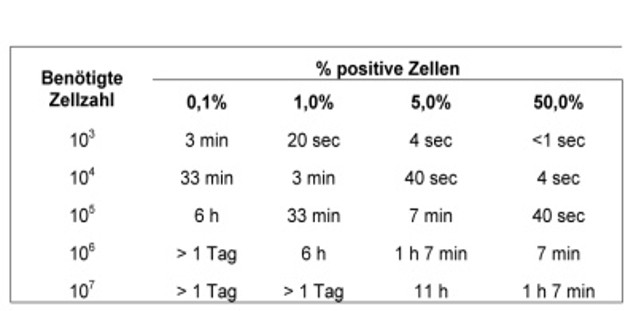
Sortdauer
Die folgenden Tabellen zeigen, wie lange ein Sortiervorgang dauert. Dies sind Mindestzeiten, ca. 20 min müssen für die Einstellung des Geräts zugerechnet werden. Die Dauer variiert mit der Größe der Zellen.
-
Sortoptionen
Folgende Sortoptionen sind mit dem FACS AriaIIIu und FACS AriaFusion möglich:
Auftrennung in bis zu 2 Populationen in 15 ml Röhrchen (am S6 bis zu 4 Populationen)
Auftrennung in bis zu 4 Populationen in FACS-Röhrchen oder Reaktionsgefäßen mit Deckel (am S6 bis zu 6 Populationen)
Ablage in Mikrotiterplatten (z.B. 96-Well)
Zugang, Sicherheit und Buchung
Vor dem Betreten der Labore ist die Teilnahme an der verpflichtenden S2 Sicherheitsunterweisung für unseren gentechnischen Anlagen erforderlich. Die Termine und auch Anmeldung zur Sicherheitsunterweisung sind in unserem Buchungssystem PPMS einzusehen und zu buchen.
Sämtliche Gerätebuchungen, Sicherheitsunterweisungen, Nutzerschulungen und die Abrechnung werden zentral über das PPMS-System verwaltet.
Die Analyzer können nach erfolgreicher Schulung und Bestätigung der Nutzungsbedingungen selbstständig verwendet werden.
Zellsortierungen werden als Service angeboten.
Bei der DFG registriert:
Serviceleistungen
- Zellsortierung mit dem FACS AriaIIIu, FACS AriaFusion und S6SE
- Sortierungen von ungetesteten humanen Proben und Bakterien (FACS AriaFusion)
- Messungen mit dem LSR Fortessa-A3, Quanteon, LSR Fortessa und Aurora
- Bestimmung von absoluten Zellzahlen am Quanteon
- Messung und Auswertung von Zellzyklen am Quanteon
- Am bildgebenden Durchflusszytometer Image Stream kann man hochauflösende Bilder mit quantifizierbaren Ergebnissen (angefärbte Marker) kombinieren.
- Analyse von Vesikeln und Micro Partikeln am Image Stream
- Bereitstellung von Auswertestationen zur selbständigen Nutzung mit folgender Software: DIVA, FlowJo, NovoExpress, Infinicyt und Ideas Software
- Einarbeitung und Unterstützung neuer Nutzer:innen an den Analysegeräten zur selbständigen Anwendung
- Schulung von Nutzer:innen mit langjähriger Durchlusszytometrie-Erfahrung an den Sortern FACS AriaIIIu, FACS AriaFusion und S6 zur selbständigen Nutzung
- Messung neuster Fluoreszenzproteine durch Anschaffung neuer Filter möglich
- Regelmäßige Lehrgänge zur Durchflusszytometrie in Zusammenarbeit mit den Geräteherstellern
- Wissenschaftliche Unterstützung: Beratung bei der Erstellung eines neuen Panels und Hilfe bei der Auswertung z.B. mit FLOWJo (buchbar in PPMS unter Tasking: Scientific Consultation)
Servicepauschalen
Die Cytometry und Cell Sorting Core Facility steht allen Forscher:innen am UKE und Interessierten zur Nutzung offen.
Es fällt eine Nutzungspauschale per Nutzungsstunde an, die auf Grundlage der benötigten Verbrauchsmittel berechnet wurde. Vierteljährlich wird die Gesamtnutzungszeit für jede:n Nutzer:in ermittelt und wahlweise über Kostenstelle oder Drittmittel abgerechnet.
Die Nutzungspauschale für UKEler:innen beträgt (Stand September 2025):
- Aurora 35 € pro Stunde
- A3 (5 Laser) 25 € pro Stunde
- LSR Fortessa (5 Laser) 25 € pro Stunde
- Quanteon 24 € pro Stunde
- LSR Fortessa (4 Laser) 22 € pro Stunde
- AriaIII 60 € pro Stunde
- AriaFusion 60 € pro Stunde
- S6SE (Spectral) 60 € pro Stunde
Kontakt
Standort CF1 (N27)
- Labor: Raum 00.068 + 068.1 > Tel. 52306 (beste Erreichbarkeit)
- Büro: Raum 0.066 > Tel. 39677
Standort HCTI (N25)
- Labor: Raum 04.2.022 + 023.2 > Tel. 50036
- Büro: Raum 04.2.037 > Tel. 39644
facs@uke.de
_3_kontaktbild.jpg)
- Wissenschaftliche Leiterin
- Cytometry and Cell Sorting Core Facility

- Technische Labormanagerin
- Cytometry and Cell Sorting Core Facility

- Senior MTLA
- Cytometry and Cell Sorting Core Facility